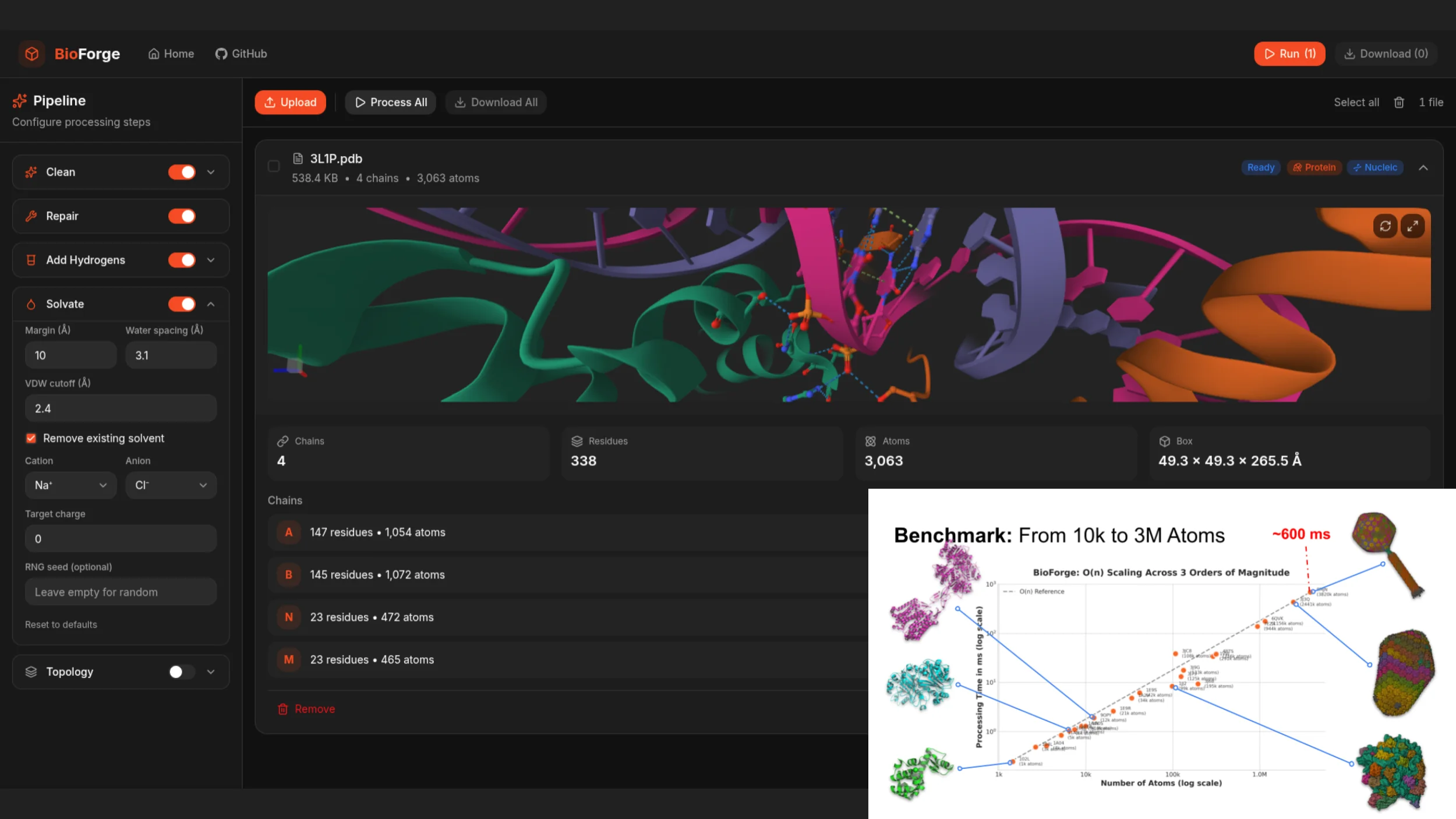
Ученик старшей школы написал на Расте движок для моделирования макромолекул и фронт на HTML/JS. Ядро
Аноним
25/02/26 Срд 00:56:14
№
1